Hochdurchsatzanalyse der Proteinadsorption an einer großen Polymerbibliothek mittels Flüssigextraktions-Oberflächenanalyse-Tandem-Massenspektrometrie (LESA-MS/MS)
Abstract
Biomaterialien spielen in der Medizin eine wichtige Rolle, von Kontaktlinsen bis hin zu Gelenkersatz. Hochdurchsatz-Screening in Kombination mit maschinellem Lernen hat synthetische Polymere identifiziert, die die Bildung bakterieller Biofilme verhindern, die Anhaftung von Pilzzellen unterbinden, die Anhaftung und den Phänotyp von Immunzellen kontrollieren oder das Schicksal von Stammzellen steuern. Die In-vitro-Präadsorption von Proteinen aus dem Kulturmedium ist entscheidend für die Kontrolle der Zellantwort. Allerdings gibt es nur wenige Studien zum Screening von Proteinadsorption in Materialbibliotheken. Wir zeigen hier, wie die quantitative Analyse der Proteinadsorption auf einem 208-gliedrigen Polymer-Microarray mittels Flüssigextraktions-Oberflächenanalyse in Kombination mit einer Adaption des Droplet-Microarray-Verfahrens (DMA) und Tandem-Massenspektrometrie (LESA-MS/MS) zur Proteinidentifizierung erreicht werden kann. In dieser Studie wird ein vollständig definiertes Zellkulturmedium mit nur vier Proteinen (Essential 8) verwendet, um die Machbarkeit des Analyseansatzes zu demonstrieren. Unsere Ergebnisse zeigen, dass wir quantitative und prädiktive Modelle des maschinellen Lernens zur Proteinadsorption generieren können, die wichtige Polymereigenschaften aufklären und den Zusammenhang zwischen Oberflächenchemie und Proteinadsorption beschreiben. Diese Informationen sind nützlich für die rationale Entwicklung neuer Materialien mit maßgeschneiderten Proteinbindungseigenschaften für Biomaterialien, medizinische Geräte oder das In-vitro-Screening von Verbindungen.
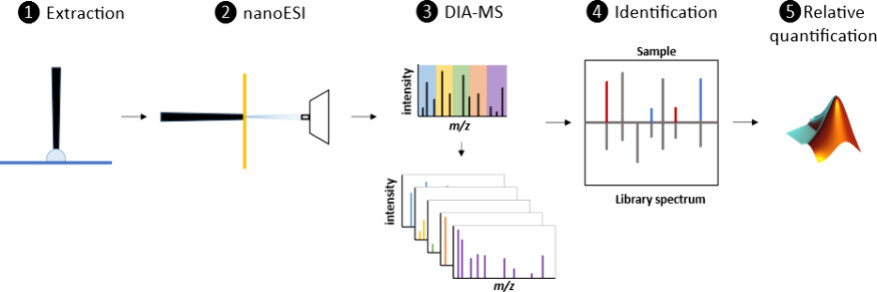
Beratung Interchim Scientific® Triversa® NanoMate® (Advion, Ithaca, NY) wurde genutzt.

